MEGAによるコロナウイルス系統樹作成 †
コロナウイルスの系統樹を描いてみよう。 †
- コロナウイルスのsmall membrane protein遺伝子(以下、E遺伝子)のサンプル配列
 E-protein.fasta を取得する。
具体的にはリンクを右クリックして、メニューから「名前を付けてリンク先を保存」を選ぶ。 E-protein.fasta を取得する。
具体的にはリンクを右クリックして、メニューから「名前を付けてリンク先を保存」を選ぶ。
- 保存先を聞いてくるので、保存したい場所に移動する。新規フォルダを作成するのもよい。たとえば、「新しいフォルダ」をクリックして新フォルダを作成し、「corona」という名前にする。
- MEGA6(またはMEGA5)を起動して、サンプル配列のアライメントを行う。
MEGA6 を起動して、「File」→「Open A File/Session」から、E-protein.fastaを選択する。
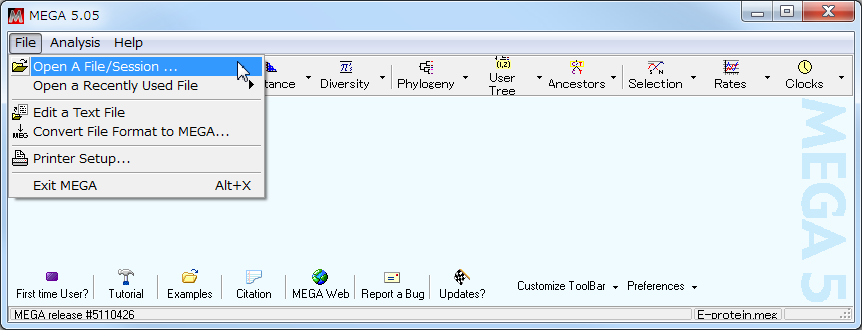
- 何をしたいか聞いてくるので、「Align」を選択する。
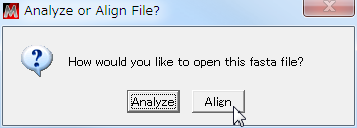
- 入力した配列をタンパク質に翻訳する。
具体的には、「Translated Protein Sequences」タブをクリックする。
(ここで使用している配列は全長がタンパク質コード領域のため、このような操作をしても問題はないが、非コード領域を含む配列を翻訳するときにはコード領域をしてやる必要がある)
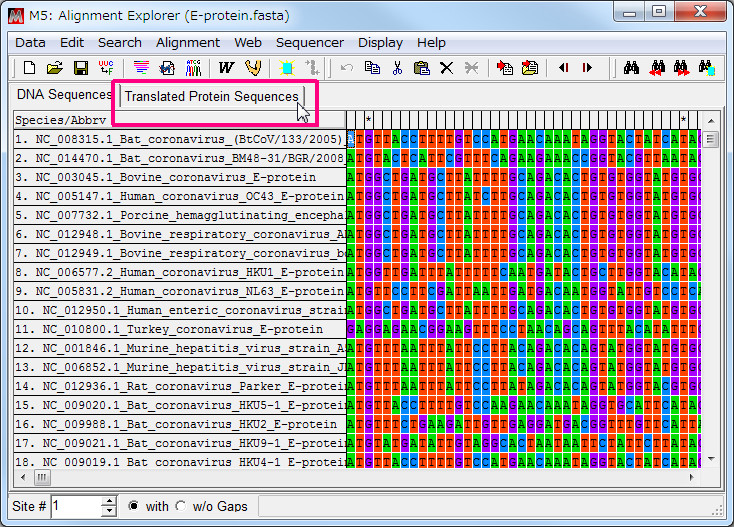
- Genetic Code について聞いてくるが、ここではそのまま「Yes」をクリックする。
- 「Alignment」→「Align by Muscle」を選ぶ。
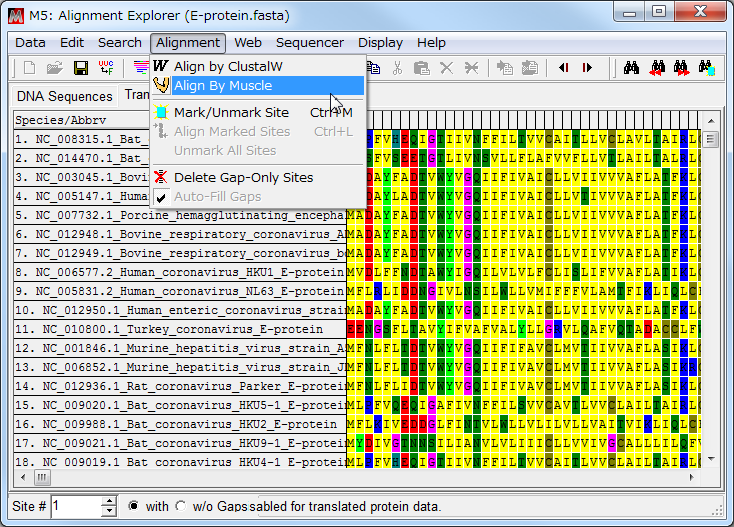
- Nothing selected for alignment. Select all?
と聞いてくるので「OK」を選択する。
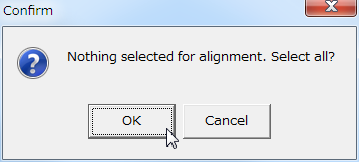
- すると、以下のようにパラメーターを聞いてくるが、そのまま「Compute」ボタンを押してアライメントを開始する。
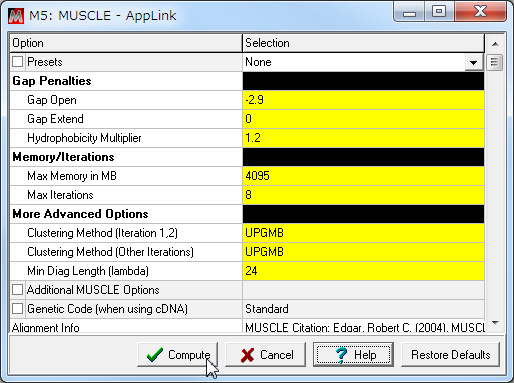
- 計算が終わったら、「Data」→「Export Alignment」→「MEGA Format」
を選択して、MEGA形式でデータを出力する。
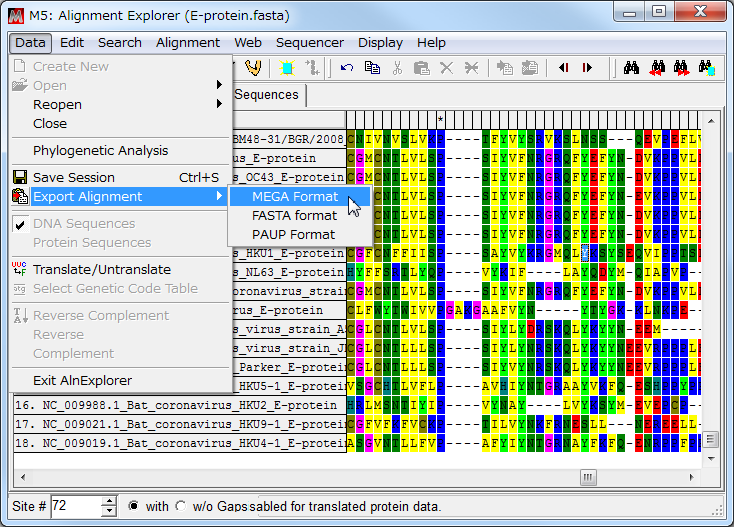
- 今回は、 E-protein_translated.meg という名前でデータを保存する。
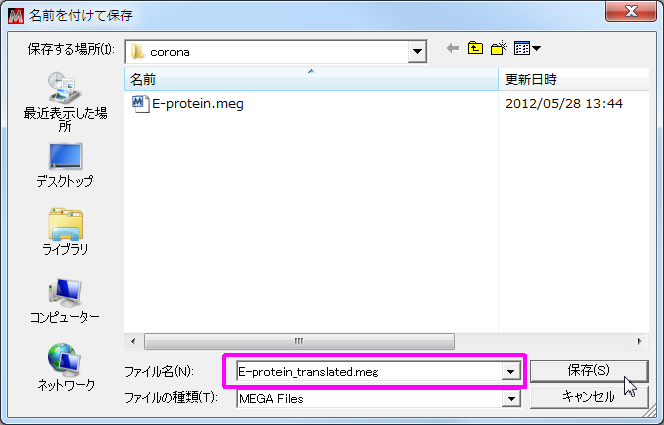
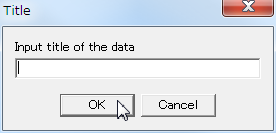
- タイトルの入力を催されるが、無視して OK を押してよい。
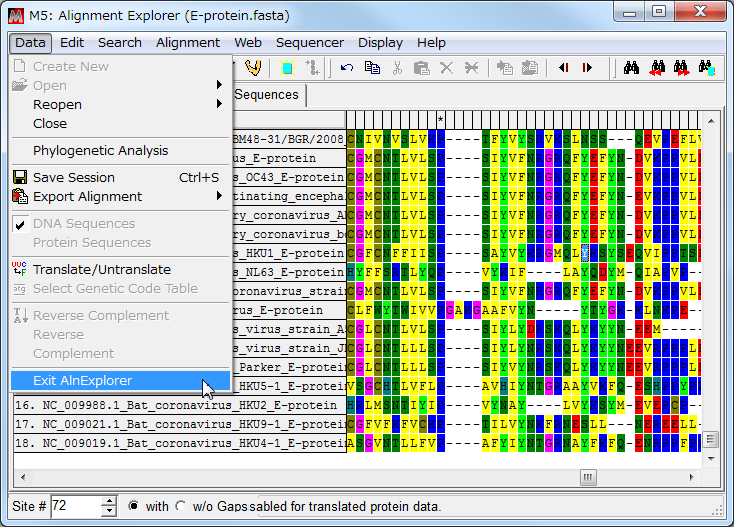
- アライメントが終了したので、「Data」→「Exit AlnExplorer」を選択して
Alignment Explorer を終了する。
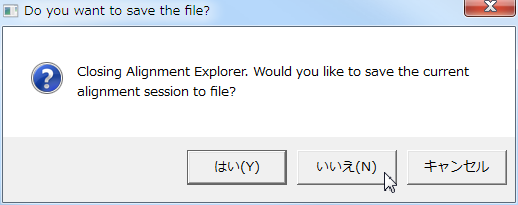
- アライメントセッションを保存するかどうか聞いてくるが、
今回は保存せずに終了したいので「いいえ」を選択する。
- 先ほど出力したMEGA形式のデータを開く。
保存先のフォルダから E-protein_translated.meg を選択してダブルクリックする。
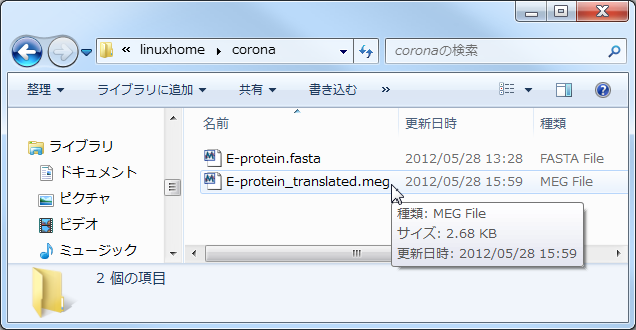
まずはBootstrap検定なしの系統樹を作成する。
- MEGAが起動したら、 「Analysis」→「Phylogeny」→ 「Construct/Test Neighbor-Joining Tree ...」を選択する。
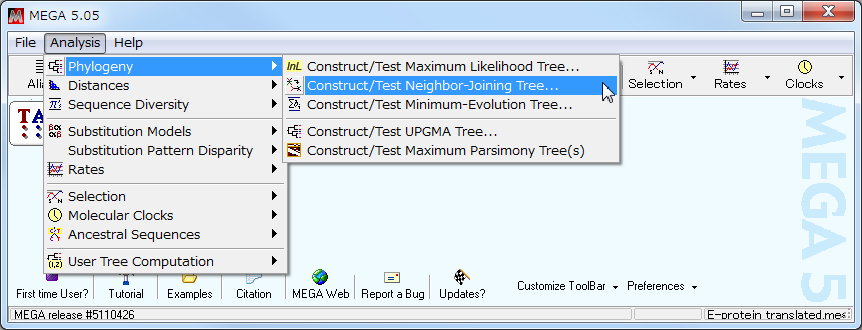
- Would you like to use the currently active data? (ファイル名)
と聞いてくるので、ファイル名を確認して「Yes」ボタンを押す。
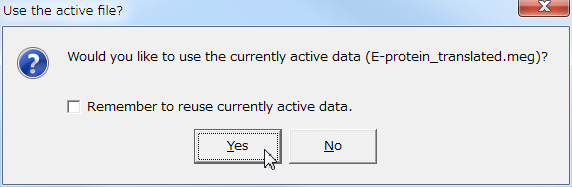
- パラメーターを聞いてくるので、「Test of Phylogeny」が「None」になっていることを確認して「Compute」ボタンを押し、計算を開始する。
- しばらく待つと系統樹ができあがる。
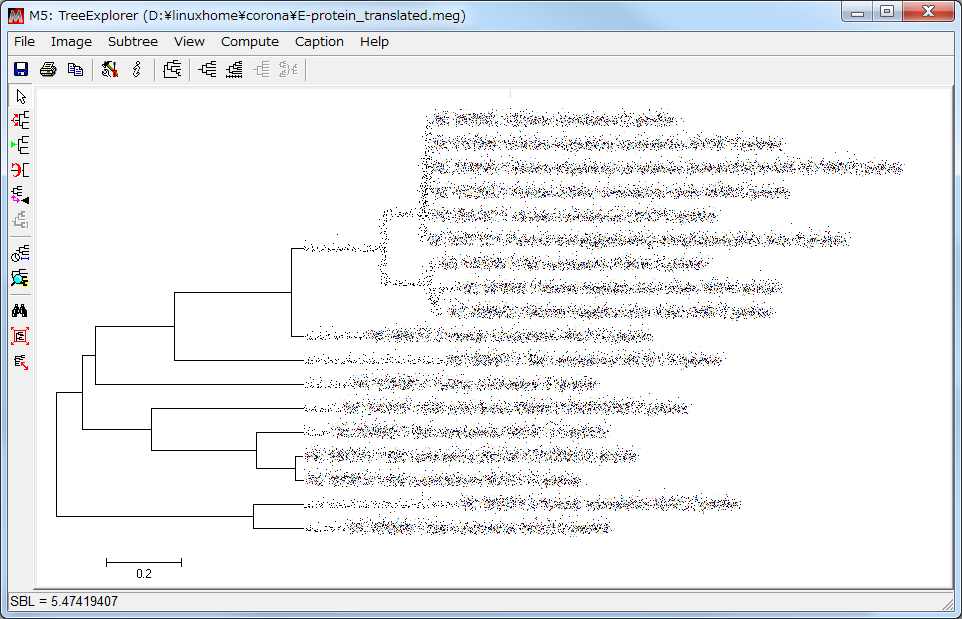
次に、Bootstrap検定をしてみる。
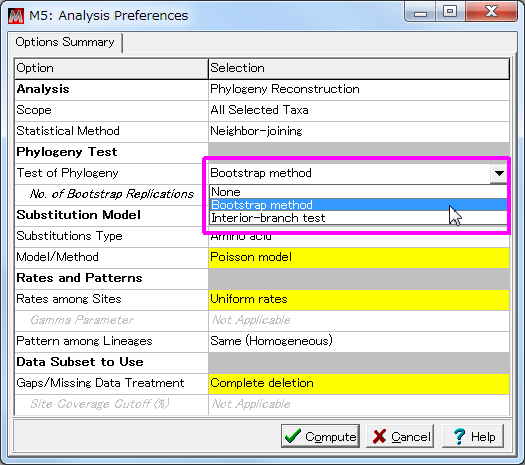
- 16からの操作を再び行い、系統樹作成のパラメーターを聞いてくる箇所で、「Test of Phylogeny」に「Bootstrap method」を選ぶ。
「No of Bootstrap Replications」が500になっていることを確認して
「Compute」ボタンを押す。
- しばらく待つと系統樹ができあがる。
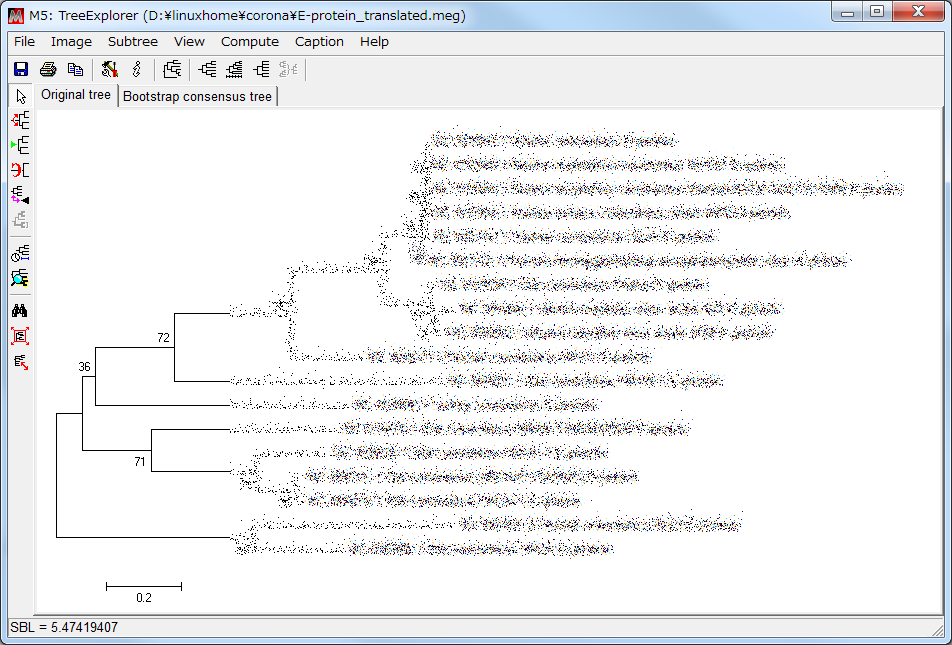
- 「Caption」を押すと図の説明や参考文献が示される。論文に図を掲載する際の助けとなる。
応用課題:構築したコロナウイルスの系統樹にSARSウイルスのデータを追加して、その系統樹を描く †
- SARSウイルスの配列
 sars_E-protein.fasta をダウンロードし、先程ダウンロードしたデータにこのデータを加えて系統樹を作成せよ。 sars_E-protein.fasta をダウンロードし、先程ダウンロードしたデータにこのデータを加えて系統樹を作成せよ。
- SARS配列を追加するには、MEGA の Alignment Explorer から追加する方法もあるが、 TeraPad などのテキストエディタで fasta 形式のファイルを開いて加工するのが簡単である。
|
![[PukiWiki] [PukiWiki]](image/pukiwiki.png)
![[PukiWiki] [PukiWiki]](image/pukiwiki.png)